Wissensgraphen beschleunigen die Suche nach neuen Wirkstoffen für Medikamente
Das erste Fraunhofer-Symposium zum Thema »Human Brain PHARMACOME« findet am 9. Juni 2021 als Online-Veranstaltung statt. Es richtet sich unter anderen an Fachleute aus Computational Biology, Pharmaindustrie und Künstlicher Intelligenz.
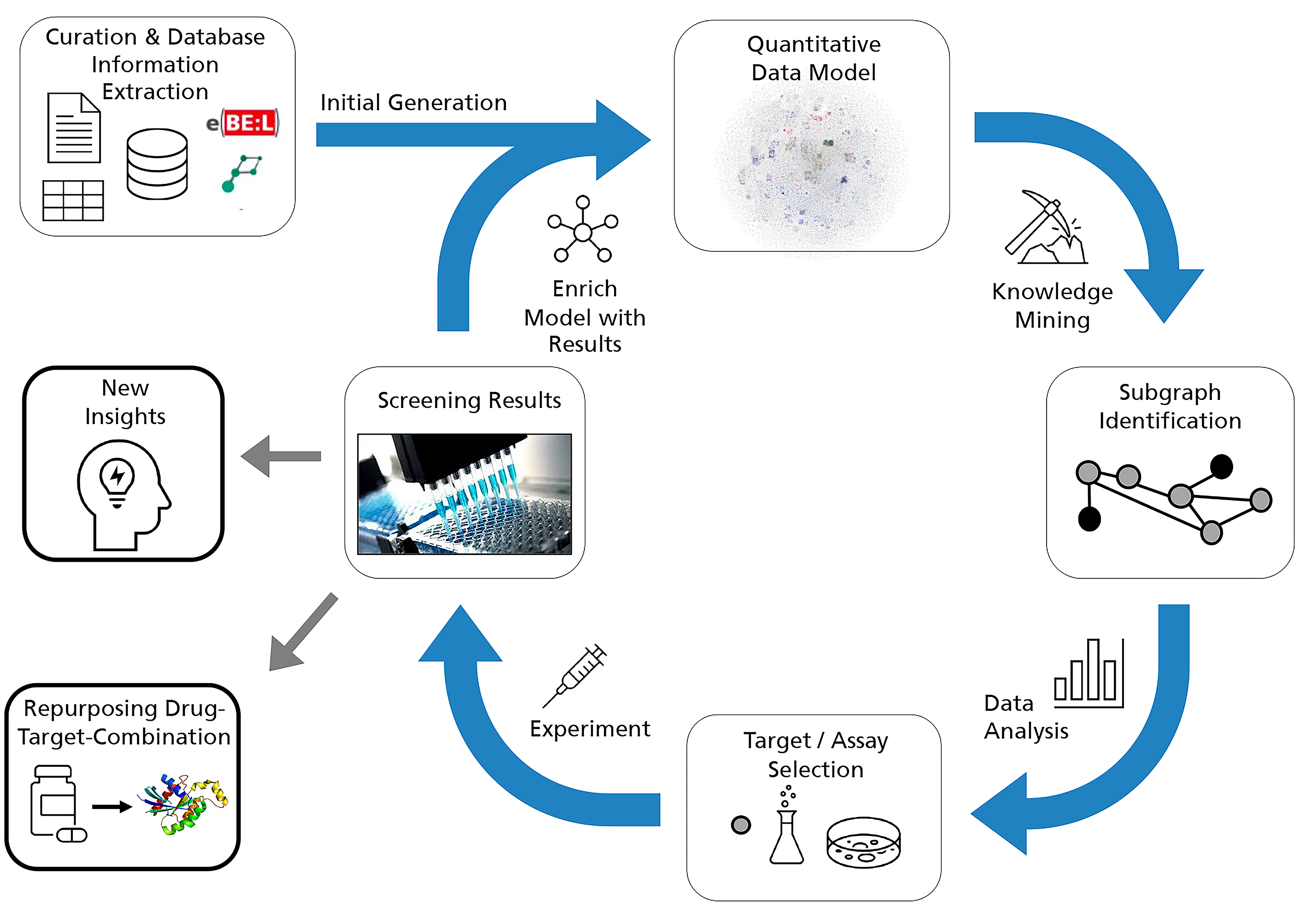
SANKT AUGUSTIN. Ein PHARMACOME stellt Daten und Wissen über biologische und chemische Prozesse sowie pathophysiologische Mechanismen in Form eines Wissensgraphen dar. Solche Wissensgraphen lassen sich am Rechner durchsuchen und interpretieren. Sie erlauben es unter anderem, neue Wirkstoffe für Medikamente schneller zu identifizieren.
Ziel des ersten Fraunhofer-Symposiums »Human Brain PHARMACOME« ist es, das Konzept dieser speziellen Wissensgraphen vorzustellen. Dabei wird beispielsweise deren Nutzen für die Identifizierung arzneimittelwirksamer pathophysiologischer Mechanismen herausgearbeitet.
»Wir verfolgen bei der Suche nach einer effektiven Präventionstherapie für Alzheimer eine radikal andere Strategie als die pharmazeutische Industrie«, sagt Prof. Dr. Martin Hofmann-Apitius. Die klassische Wirkstoffentwicklung, so der Leiter des Geschäftsfelds Bioinformatik bei Fraunhofer SCAI, gehe typischerweise von einer einzigen Hypothese zur Krankheitsentstehung aus und scheitere damit etwa in der Demenzforschung seit Jahren. »Wir starten dagegen mit einer Vielfalt von Krankheitsmechanismen, die als Modelle im Rechner vorliegen und es erlauben, Daten und Wissen gegeneinander abzugleichen und mit Simulationen zu verknüpfen.« Das Ergebnis dieses holistischen Ansatzes ist ein mechanistisches Modell aller im menschlichen Gehirn aktiven Substanzen, ihrer ‚Targets‘ und Wirkmechanismen.
Themen der Vorträge sind
- Verwendung von Informationsextraktionstechnologien für wissenschaftliche Publikationen und Patenten,
- »Text-to-Graph«-Technologien und dynamische Datenfusion für die PHARMACOME-Generierung,
- Anwendungen KI-basierter Netzwerkalgorithmen und BiK>Mi, einer speziellen PHARMACOME-Benutzeroberfläche, zur Identifizierung von Pathophysiologie-Mechanismen, die für ein Targeting geeignet sind,
- Entwicklung neuartiger Strategien für High-Throughput- und High-Content-Screening und experimentelle Validierung von In-Silico-Hypothesen und
- Nutzung von PHARMACOMEs für zukünftige Drug-Targeting- und Drug-Repurposing-Ansätze (etwa Proximity-Drug-Strategien).
Anmeldung und weitere Informationen finden Sie hier.